近日,中國科學院-馬普計算生物學研究所楊力研究組與上海科技大學陳佳研究組、楊貝副研究員開展合作研究,利用共表達尿嘧啶糖苷酶抑制劑(uracil DNA glycosylase inhibitor, UGI)的方法,開發了一種基于堿基編輯器3(base editor 3, BE3)的增強型堿基編輯器(enhanced base editor, eBE),實現了更高準確度的基因組單堿基編輯。相關成果“Enhanced base editing by co-expression of free uracil DNA glycosylase inhibitor”,于8月29日在知名學術期刊《細胞研究》(Cell Research)上在線發表。
近年內興起的CRISPR/Cas9基因編輯技術利用可設計的Cas9核酸酶通過堿基插入、缺失或替換等方式,對生物體基因組DNA特定片段進行改造,進而實現對靶基因的編輯。傳統的CRISPR/Cas9基因編輯技術雖然具有較高的基因敲除效率,但其在執行堿基替換(對譬如基因突變進行矯正)的效率通常很低,這也限制了CRISPR/Cas9基因編輯工具從科研向應用的全面轉化。近期發展出的堿基編輯(base editing)系統,由CRISPR/Cas9和APOBEC胞嘧啶脫氨酶兩個獨立的體系整合而成,可在基因組靶向位點實現由胞嘧啶(cytosine, C)向胸腺嘧啶(thymine, T)的編輯改造(Komor et al., Nature?2016)。其中,BE3雖然實現了較高的C至T編輯效率,但是也伴隨著較高水平的非目的性堿基插入或缺失(insertion/deletion, indel)和C至A或G的編輯副產物,這些都顯著地降低了堿基編輯器在基礎研究和臨床上的深入應用。在這項最新的研究中,科研人員在前期對BE3導致非目的性突變機制探索的基礎上,利用共表達UGI的方法,成功開發出了增強型基因組堿基編輯器-eBE。利用多種UGI與BE3共表達的策略,eBE實現了更高精度和更高效率的堿基編輯,為堿基編輯技術在基礎研究及未來臨床領域的深入應用提供了新方法和新思路。
楊力研究員長期從事組學系統生物學和計算生物學研究。該項最新研究成果在陳佳教授、楊力研究員和楊貝副研究員的共同指導下,由楊力研究組研究助理薛尉和上科大2015級研究生王麗潔、嚴磊作為共同第一作者主要完成。該項研究得到自國家自然科學基金委、科技部、上海市科委和上科大科研啟動基金的共同支持。
論文鏈接:https://doi.org/10.1038/cr.2017.111
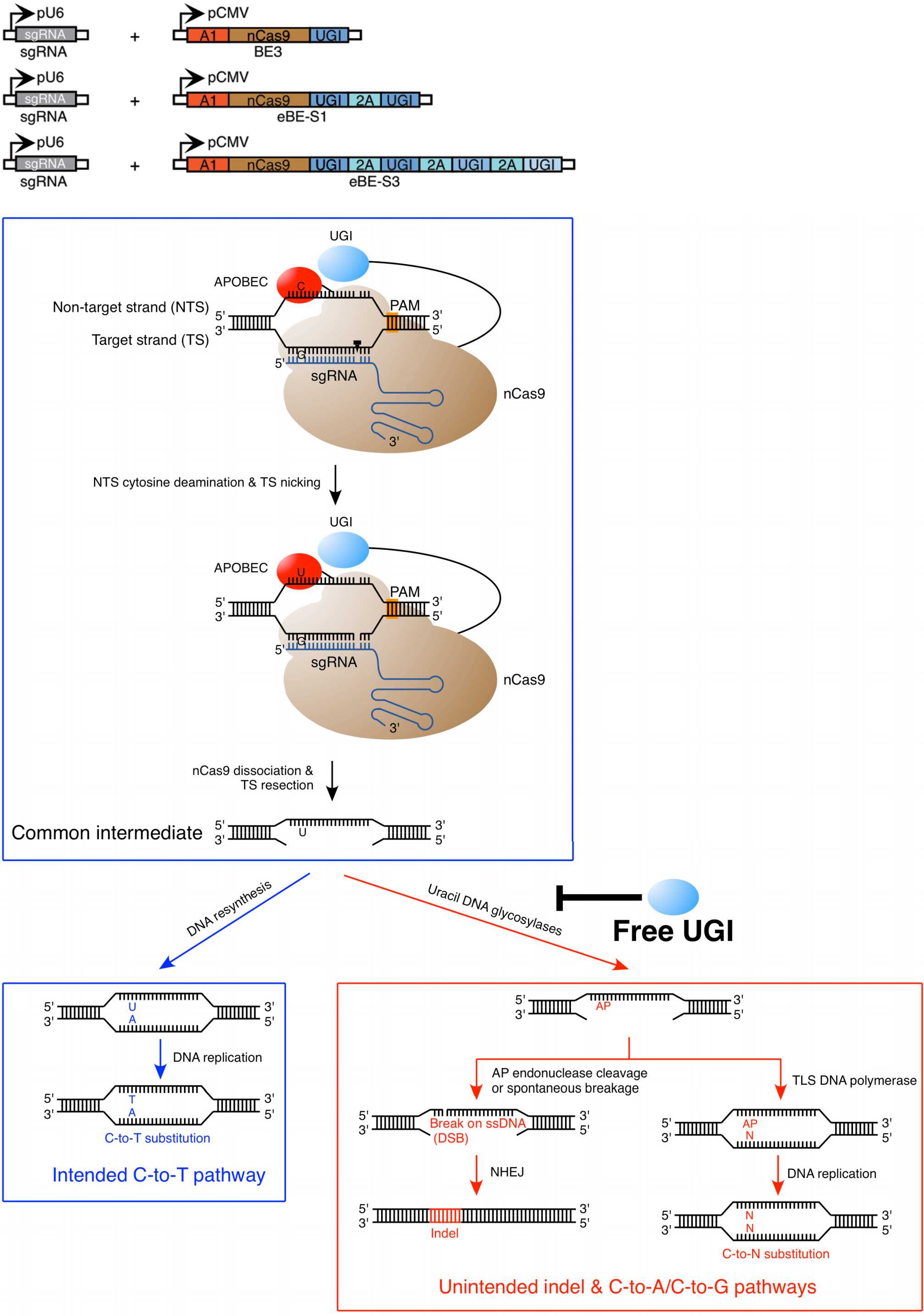
圖.增強型堿基編輯系統模式圖