中國科學(xué)院上海生命科學(xué)研究院(營養(yǎng)與健康院)中國科學(xué)院-馬普計算生物學(xué)研究所楊力研究組與上海科技大學(xué)生命學(xué)院陳佳研究組和黃行許研究組通過合作,成功開發(fā)出一系列基于人胞嘧啶脫氨酶APOBEC的新型普適堿基編輯器,其中基于人APOBEC3A(hA3A)的堿基編輯器可高效介導(dǎo)甲基化胞嘧啶mC到胸腺嘧啶T的編輯。相關(guān)成果以“Efficient base editing in methylated regions with a human APOBEC3A-Cas9 fusion”為題,于當?shù)貢r間2018年8月20日在線發(fā)表在國際知名學(xué)術(shù)期刊《自然-生物技術(shù)》(Nat Biotechnol)上。
近年來,將CRISPR/Cas基因編輯酶(如CRISPR/Cas9、CRISPR/Cpf1等)與核酸脫氨編輯酶(如胞嘧啶脫氨酶APOBEC/AID、腺嘌呤脫氨酶ADAR等)整合發(fā)展出的堿基編輯系統(tǒng)(Base Editor, BE),可在單堿基水平實現(xiàn)高效率的靶向基因編輯(C-to-T、A-to-G)。這種新型堿基編輯系統(tǒng)理論上可對數(shù)百種引起人類疾病的基因組單堿基突變進行定點矯正,因此擁有巨大的臨床應(yīng)用潛力。堿基編輯技術(shù)于2017年被Science雜志評為全球十大年度科學(xué)突破之一,進一步凸顯出該領(lǐng)域在科學(xué)研究和臨床應(yīng)用上的重要潛力。
在這項最新的研究中,合作團隊首先利用生物信息學(xué)方法系統(tǒng)分析了與人類疾病相關(guān)的單堿基突變,發(fā)現(xiàn)胸腺嘧啶T到胞嘧啶C突變中的大部分處于CpG二核苷酸位點。而在哺乳動物基因組中,CpG位點的胞嘧啶通常易被甲基化修飾。目前已報導(dǎo)的堿基編輯系統(tǒng)大多是利用大鼠APOBEC1(rA1)作為脫氨酶進行基因組編輯,合作團隊的研究發(fā)現(xiàn)此類rA1依賴的堿基編輯通常會受到DNA甲基化修飾水平的影響,因此在基因組DNA高甲基化區(qū)域無法實現(xiàn)高效的堿基編輯。為了實現(xiàn)高甲基化區(qū)域內(nèi)的高效堿基編輯,合作團隊成員利用十余種來自不同物種的APOBEC胞嘧啶脫氨酶家族蛋白構(gòu)建出一系列新型堿基編輯器,可廣泛用于胞嘧啶C至胸腺嘧啶T單堿基編輯。更為重要的是,合作團隊通過一系列篩選鑒定,發(fā)現(xiàn)基于人APOBEC3A的堿基編輯器(hA3A-BE)可在基因組高甲基化區(qū)域?qū)崿F(xiàn)高效的甲基化胞嘧啶mC至胸腺嘧啶T單堿基編輯。深入研究發(fā)現(xiàn),hA3A-BE是一種普適且高效的堿基編輯器,可在已檢測的多種環(huán)境中實現(xiàn)胞嘧啶C(或甲基化胞嘧啶mC)至胸腺嘧啶T的高效編輯。最后,通過對人APOBEC3A的系統(tǒng)性改造,研究團隊縮小了hA3A-BE的編輯區(qū)間,進一步提高了其堿基編輯的精度。與之前報道的基于大鼠APOBEC1的堿基編輯器相比,基于人APOBEC3A的新型堿基編輯器應(yīng)用范圍更加廣泛和全面,這為堿基編輯系統(tǒng)在基礎(chǔ)研究及未來臨床領(lǐng)域的全面深入應(yīng)用提供了新工具、新方法和新思路。
楊力研究組長期從事核酸系統(tǒng)生物學(xué)及相關(guān)新技術(shù)拓展研究(http://yang-laboratory.com)。此前通過合作已闡明APOBEC胞嘧啶脫氨酶在CRISPR/Cas9介導(dǎo)的基因編輯過程中產(chǎn)生突變的分子機制(Lei et al., Nat Struct?Mol?Biol?2018);成功創(chuàng)建增強型Cas9堿基編輯器(Wang et al., Cell Res?2017);發(fā)展了可在基因組A/T富集區(qū)域內(nèi)開展有效編輯的Cpf1堿基編輯器(Li et al., Nat?Biotechnol?2018);并應(yīng)邀撰寫RNA單堿基編輯的研究觀點論文(Yang and Chen, Science?2017)。
該工作在楊力研究員、陳佳教授、黃行許教授的共同指導(dǎo)下完成,得到了國家自然科學(xué)基金委、科技部、上海市科委和上科大科研啟動基金的支持。上海科技大學(xué)生命學(xué)院陳佳研究組2016級碩博連讀研究生王瀟、黃行許研究組2015級碩博連讀研究生李佳楠、免化所楊貝博士和中國科學(xué)院計算生物學(xué)研究所楊力研究組2015級碩博連讀研究生王瀅和研究助理韋佳為同等貢獻共同第一作者。該研究使用的高通量測序數(shù)據(jù)由PICB Omics Core完成,并儲存于NCBI (GEO:GSE114999)和PICB大數(shù)據(jù)中心(National Omics Data Encyclopedia:OEP000030)。
原文鏈接:https://doi.org/10.1038/nbt.4198
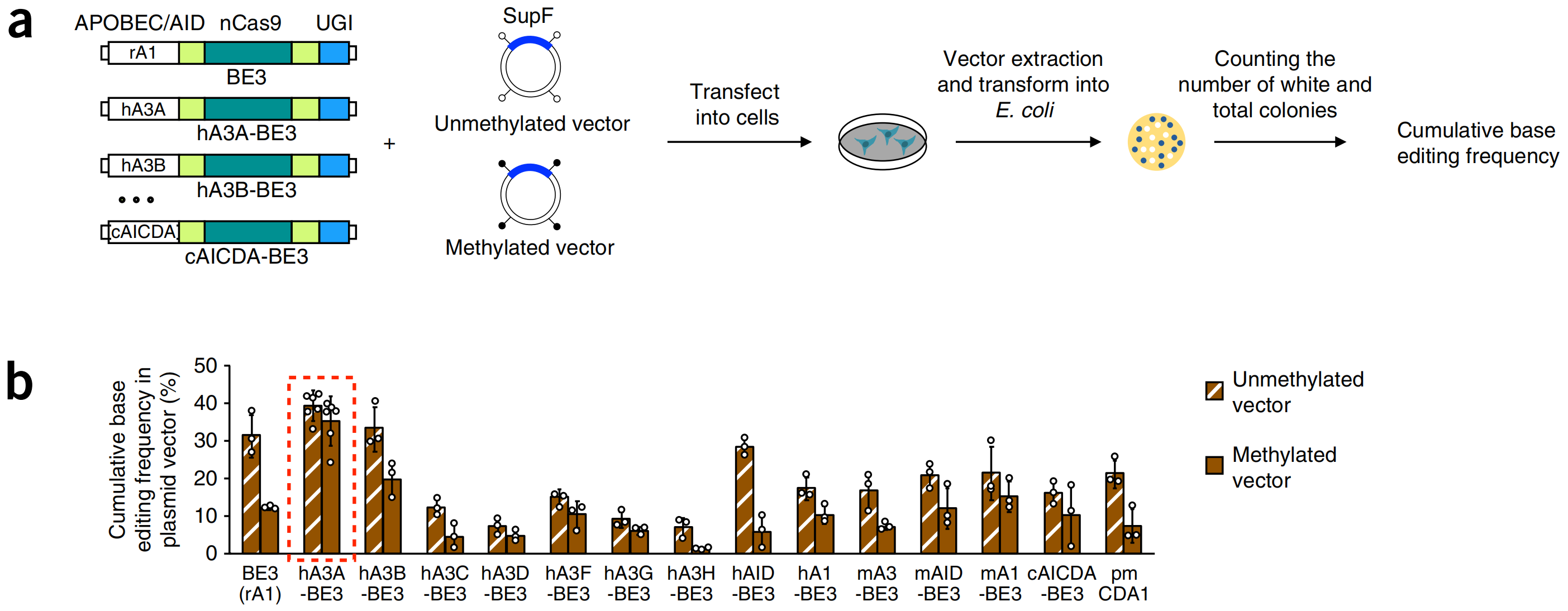
圖: 篩選構(gòu)建可實現(xiàn)甲基化mC-to-T的新型堿基編輯器。
(a)構(gòu)建多種堿基編輯器并篩選其在高甲基化區(qū)域的編輯效率。(b)基于人APOBEC3A的堿基編輯器(hA3A-BE3)能夠在高甲基化區(qū)域進行高效堿基編輯。