11月30日,國際學術期刊Nature Methods發表了中國科學院上海營養與健康研究院計算生物學研究所Andrew Teschendorff研究組的研究論文“Identification of differentially methylated cell types in epigenome-wide association studies”,報道了一種新的有助于識別與疾病相關的表觀遺傳通路的“CellDMC”統計算法,“破解”了表觀全基因組關聯分析中的關鍵難點。
DNA甲基化(DNAm)是DNA的共價修飾,其可以調節基因活性,并且易受到疾病風險因子的影響。表觀全基因組關聯分析(EWAS)的主要目標是測量大量個體中全基因組DNA甲基化,鑒定與疾病風險相關的DNA甲基化變化。然而,這一過程的主要障礙之一是細胞類型異質性:EWAS所使用的組織是不同細胞類型的復雜混合物,每種細胞類型具有其特有的DNA甲基化譜,因此可能產生錯誤的分析結論。到目前為止,尚無有效手段來確定驅使DNA甲基化發生變化的細胞類型和表觀遺傳通路。
在Andrew Teschendorff研究員的指導下,博士生鄭世杰等人開發了一種名為“CellDMC”的新型統計算法,該算法不僅能夠確定特定基因組位點的變化,而且能夠確定導致這些DNA甲基化變化的細胞類型。相較于當前無法識別DNA甲基化變化的通用方法,這種算法對于DNA甲基化變化的識別靈敏度超過90%。隨后研究人員利用幾個真實EWAS數據進行算法測試,結果表明類風濕性關節炎相關的大量DNA甲基化變化發生于一種特定的血細胞亞型(B細胞),這種B細胞的改變在該疾病的發生機制中特別重要。在另一個測試中,該算法識別了暴露于煙霧致癌物質的正常細胞和肺癌祖源細胞中的DNA甲基化變化,從而有助于將吸煙有關的表觀遺傳通路與肺癌進行關聯。
值得一提的是,EWAS中有一些昂貴且難以實現的技術,如細胞分選技術,單細胞甲基化組測序技術。CellDMC可幫助EWAS的研究人員識別疾病相關細胞類型的改變,而無需使用這些技術。檢測疾病相關和疾病風險相關的細胞類型改變的能力,對于鑒定和開發表觀遺傳疾病風險生物標志物,以及實現P4醫學目標具有重要意義。
上述研究得到了國家自然科學基金委員會(31571359;?31771464; 31401120)和中國科學院的資助。
原文鏈接:https://www.nature.com/articles/s41592-018-0213-x
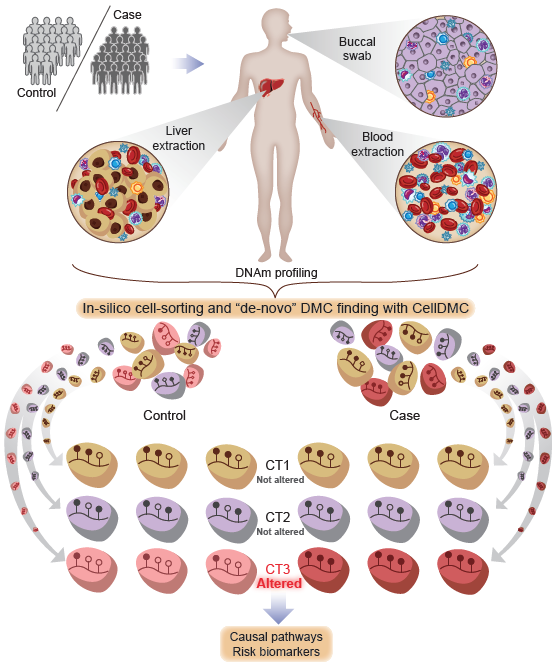
圖. CellDMC識別差異化甲基化的細胞類型