2020年9月4日,國際學術期刊Genome Biology在線發表了中國科學院上海營養與健康研究所Andrew Teschendorff研究組題為“EPISCORE: cell-type deconvolution of bulk tissue DNA methylomes from single-cell RNA-Seq data”的最新研究成果,該研究報道了一種新型算法——EPISCORE,是一種可以應用于任意組織類型的表觀基因組單細胞解析算法。
DNA甲基化是發生在DNA上的共價修飾,作為一種重要的表觀遺傳類型,DNA甲基化受多種疾病及風險因子的影響,與疾病的發生和發展有潛在的因果關系,并有望作為疾病診斷的一種新型生物分子標記物。但是,由于實驗成本和條件的限制,大量的DNA甲基檢測一般只在混合了多種細胞類型的復雜組織中進行,得到的是多個不同細胞類型DNA甲基化變化的平均值,難以用來統計不同細胞類型中DNA甲基化的功效及其生物學解釋。因此,領域內迫切需要開發一種高效的計算生物學研究方法,能夠在單細胞層面解析復雜組織中的差異DNA甲基化組。
近期,中國科學院上海營養與健康研究所Andrew Teschendorff研究員指導的研究團隊開發了一種名為“EPISCORE”的新型算法,用以從單細胞RNA-Seq中分析獲得給定組織類型中的各種細胞類型,并從中發現蘊含與疾病發生相關DNA甲基化變化的特定細胞類型。EPISCORE算法利用了組織特異性單細胞RNA-Seq圖譜數據(比如Human Cell Atlas Consortium)的強大功能和高分辨率特性,基于細胞類型特異性標記物的DNA甲基化差異特性,有效地將組織特異性mRNA表達圖譜轉化為單細胞分辨率的組織特異性DNA甲基化圖譜。利用EPISCORE算法對肺癌數據開展研究,成功揭示了肺癌內皮細胞中的DNA甲基化表觀遺傳改變,提示表皮細胞向間充質細胞的轉化過程是癌細胞入侵和轉移的基礎。
由于大多數公開的DNA甲基化數據源自于混合了多種細胞類型的復雜組織樣本,因此無法發揮其作為疾病診斷分子標志物的潛力。EPISCORE的開發則使得科研人員能夠重新分析這些公開發表的表觀遺傳數據集,在精確獲得復雜組織樣本中不同細胞類型比例的基礎上,進一步在單細胞水平鑒定細胞特異性的DNA甲基化變化,對闡明表觀遺傳變化在疾病發生和發展中的因果作用具有重要意義。此外,EPISCORE算法低成本的特點使它成為單細胞甲基化組學分析的有效替代方法。而且,區別于單細胞甲基化組學分析,EPISCORE算法可應用于任意組織類型的EWAS(表觀基因組關聯分析)研究。
中國科學院上海營養與健康研究所Andrew Teschendorff研究員為該論文的通訊作者,Andrew Teschendorff研究員和博士研究生朱天余為該研究的共同第一作者。該研究得到了中國科學院和國家自然科學基金委項目資助,項目批準號分別為31571359,31771464和31970632。(科技處)
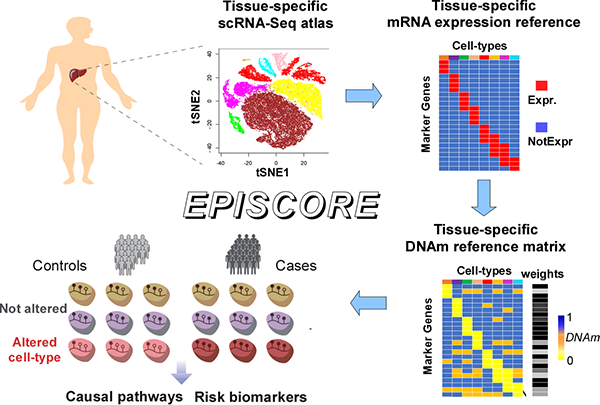
圖. EPISCORE算法流程圖
原文鏈接:https://genomebiology.biomedcentral.com/articles/10.1186/s13059-020-02126-9